Le dot plot, également connu sous le nom de diagramme à points ou à bandes, est un outil graphique puissant et polyvalent utilisé dans divers domaines, notamment en biologie computationnelle et en statistique. Bien qu'il puisse sembler rudimentaire, sa simplicité masque sa capacité à révéler des motifs complexes dans les données, en particulier lorsqu'il s'agit de comparer des séquences biologiques. Cet article explore la nature, l'application et l'interprétation des dot plots dans le contexte de la réplication biologique et de l'alignement séquentiel, en utilisant les informations fournies pour construire une compréhension approfondie.
Qu'est-ce qu'un Dot Plot ?
Un dot plot est fondamentalement une méthode de visualisation qui compare deux ensembles de données, ou une séquence avec elle-même, en plaçant l'une des séquences horizontalement et l'autre verticalement sur une grille. Lorsqu'un élément (par exemple, une base nucléotidique ou un acide aminé) d'une séquence correspond à l'élément à la même position dans l'autre séquence, un point est dessiné à l'intersection correspondante de la grille. L'accumulation de ces points forme des lignes qui représentent les similitudes entre les séquences.

Dans le domaine de la bioinformatique, un dot plot est une méthode graphique pour comparer deux séquences biologiques et identifier les régions de similitude étroite après un alignement de séquences. C'est l'une des techniques de comparaison les plus anciennes, mais elle reste très efficace pour les comparaisons globales. Il s'agit de placer l'une des séquences horizontalement, l'autre verticalement, formant ainsi une matrice. La similarité entre deux séquences protéiques ou d'acides nucléiques peut être visualisée à l'aide d'une matrice de similarité, connue sous le nom de dot plot.
Contrairement aux diagrammes de dispersion, qui représentent des paires de valeurs numériques, les dot plots sont plus similaires à des histogrammes qui trient les informations en "bacs" (catégories). Chaque point représente une valeur, et la taille de chaque "barre" de points est équivalente au nombre d'éléments dans une catégorie spécifique. Un exemple simple serait la sélection des aliments consommés en collation par un groupe de personnes. Si tout le monde a choisi la pizza, un point sera placé au-dessus de "pizza" pour chaque personne. Si trois autres personnes ont ajouté un hamburger, trois points seront ajoutés à la colonne "hamburger".
Applications en Biologie Moléculaire
En biologie, les dot plots sont particulièrement utiles pour visualiser les relations entre des séquences d'ADN, d'ARN ou d'acides aminés. Ils permettent de détecter rapidement des caractéristiques telles que les répétitions, les duplications, les délétions, les insertions et les inversions au sein d'une séquence ou entre deux séquences différentes.
Comparaison de Séquences : Auto-comparaison et Comparaison Croisée
Un dot plot peut être utilisé pour comparer une séquence avec elle-même (auto-comparaison) ou pour comparer deux séquences différentes (comparaison croisée).
Auto-comparaison : Lorsqu'une séquence est comparée à elle-même, la diagonale principale représente la correspondance parfaite de chaque position avec elle-même. Des lignes parallèles à cette diagonale indiquent des régions répétitives ou des duplications au sein de la séquence. Par exemple, trois lignes parallèles pourraient indiquer trois copies d'une région répétée.
Comparaison Croisée : La comparaison de deux séquences distinctes permet d'identifier les régions d'homologie, c'est-à-dire les parties qui partagent une origine évolutive commune. Les lignes diagonales dans ce cas indiquent des segments de similitude entre les deux séquences.
Interprétation des Motifs dans un Dot Plot
L'interprétation des motifs formés par les points sur un dot plot est cruciale pour comprendre les relations entre les séquences.
La Diagonale Principale : Une ligne diagonale nette et continue indique une similitude élevée entre les deux séquences, position par position. Dans le cas d'une auto-comparaison, cela signifie que la séquence est très conservée. Dans une comparaison croisée, cela suggère une forte homologie entre les deux séquences.
Lignes Parallèles à la Diagonale : La présence de plusieurs lignes parallèles à la diagonale principale est un signe clair de répétitions ou de duplications. Dans une auto-comparaison, comme mentionné précédemment, cela indique des régions répétées au sein d'une seule séquence. Pour une comparaison croisée, des lignes parallèles peuvent signifier que des régions répétées dans une séquence correspondent à des régions répétées dans l'autre.

Régions Hautement Répétitives : Dans des cas extrêmes, des régions hautement répétitives peuvent apparaître comme de nombreuses petites lignes parallèles formant une sorte de carré ou de bloc dense sur le graphique.
Délétions : Une délétion dans l'une des séquences par rapport à l'autre se manifeste par un "saut" latéral sur la ligne diagonale principale. La ligne s'interrompt et reprend plus loin, créant un décalage.
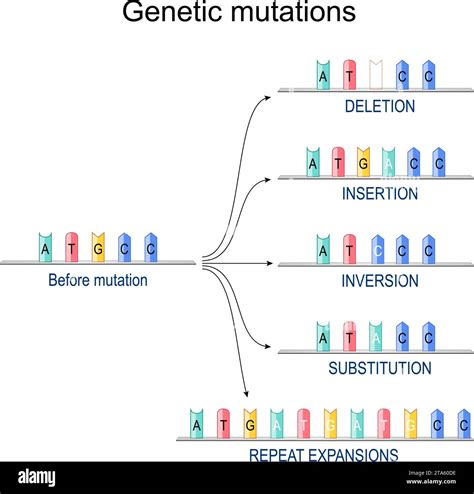
Insertions : Inversement, une insertion dans l'une des séquences, qui n'a pas de correspondance dans l'autre, provoque un "saut" vertical (ou horizontal, selon l'axe) sur la ligne principale. La ligne monte (ou descend) puis reprend sa course, indiquant un segment manquant dans l'autre séquence.
Inversions : Une inversion, où une partie d'une séquence est inversée, apparaît comme une ligne diagonale dirigée dans la direction opposée à la diagonale principale. Si la diagonale principale va du coin inférieur gauche au coin supérieur droit, une inversion sera représentée par une ligne allant du coin supérieur gauche au coin inférieur droit. Ces inversions sont souvent colorées en rouge dans certains outils pour une meilleure visibilité.
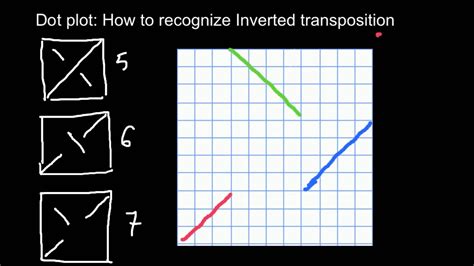
Différences Structurelles : Les insertions et les délétions, collectivement appelées indels, ainsi que les mutations (qui entraînent des décalages ou des discontinuités), peuvent entraîner des configurations de lignes multiples et variées. Les régions de faible complexité, caractérisées par la redondance de quelques acides aminés, peuvent également influencer l'apparence du dot plot, parfois de manière à créer du "bruit" visuel.
Les Outils pour Créer et Analyser des Dot Plots
La création et l'analyse de dot plots ont évolué au fil du temps, avec le développement de divers outils logiciels.
Première Génération d'Outils : Ligne de Commande
Les premiers outils étaient principalement basés sur la ligne de commande et produisaient des graphiques statiques. Ils comprenaient des programmes comme tupple_plot et dot-matrix. Ces outils impliquaient généralement deux étapes : la génération d'un fichier de correspondances, suivi du rendu graphique. Ils étaient souvent limités aux fichiers FASTA uniques et ne permettaient pas d'interaction avec le graphique résultant. De plus, certains étaient spécifiques à des systèmes d'exploitation comme Unix.
Deuxième Génération d'Outils : Interfaces Graphiques et Plateformes Indépendantes
Le développement de logiciels en Java a permis la création d'outils plus conviviaux et indépendants de la plateforme. Des exemples incluent JDotter, Gepard et r2cat. Ces outils ont introduit des fonctionnalités interactives, permettant aux utilisateurs de manipuler l'orientation et l'ordre des séquences pour optimiser l'alignement sur la diagonale et faciliter la comparaison visuelle. Cependant, ces outils pouvaient encore avoir des limitations quant à la taille des séquences qu'ils pouvaient traiter efficacement ; par exemple, Gepard pouvait prendre plus d'une heure pour aligner des chromosomes humains.
Troisième Génération d'Outils : Visualisation Web et Traitement de Grands Génomes
La génération la plus récente d'outils de dot plot utilise des bibliothèques JavaScript et est souvent accessible via des interfaces web. Ces outils sont conçus pour traiter de très grands ensembles de données, tels que des génomes entiers, en des temps raisonnables.
Un exemple notable est D-GENIES. Ce programme, accessible en ligne ou en version autonome, exploite des aligneurs modernes comme minimap2 pour comparer des séquences multi-FASTA volumineuses et potentiellement peu similaires. Pour gérer la consommation de mémoire et le temps de traitement, D-GENIES divise les grandes séquences (comme les chromosomes) en blocs de dix méga-bases qui sont ensuite alignés individuellement. Les alignements contigus de ces blocs sont visuellement fusionnés dans le graphique.
D-GENIES offre une interface utilisateur graphique riche en fonctionnalités :
- Navigation et Visualisation : Permet de lancer de nouveaux alignements, de visualiser les tracés, de parcourir une galerie d'exemples et de consulter la documentation.
- Configuration de l'Alignement : Les utilisateurs peuvent télécharger des fichiers FASTA ou fournir des URL. Les fichiers peuvent être compressés en gzip. Si aucun fichier de requête n'est fourni, la référence est alignée sur elle-même, et les correspondances triviales (même séquence, même position) sont supprimées.
- Interactivité : Le dot plot généré est interactif. Les utilisateurs peuvent zoomer sur des régions spécifiques en cliquant sur des carrés ou en utilisant la molette de la souris. Des options permettent de modifier le schéma de couleurs (adapté aux utilisateurs daltoniens), de filtrer les correspondances par similarité et taille, de modifier la largeur des lignes et des bordures, et de trier les séquences de requête par rapport à la référence.
- Exportation : Les graphiques peuvent être exportés en formats PNG et SVG, adaptés à la publication. Des fichiers d'alignement (PAF, MAF) et des fichiers FASTA ordonnés ou désordonnés peuvent également être téléchargés.
- Gestion du Bruit : D-GENIES intègre des algorithmes pour identifier et filtrer le "bruit", c'est-à-dire les correspondances de petite taille et de haute fréquence qui peuvent masquer les motifs importants.
- Fonctionnalités Avancées : Des options comme "Strong precision" réduisent les bordures des correspondances pour éliminer les petits segments, révélant ainsi davantage les discontinuités. L'orientation de la séquence de requête peut être inversée par un clic droit.
- Résumé de Similarité : Un bouton "Summary" génère un graphique linéaire présentant le profil de similarité de la référence, une somme des projections des correspondances sur la référence par catégorie de similarité.
L'intégration de nouveaux algorithmes d'alignement et de bibliothèques de visualisation JavaScript de pointe a permis le développement de cette troisième génération d'applications de dot plot. Ces outils sont capables de traiter de grands génomes dans des délais raisonnables, tout en offrant des interfaces graphiques conviviales. La capacité de D-GENIES à être étendu avec de nouveaux aligneurs et formats de fichiers d'alignement témoigne de la flexibilité de cette approche.
Dot Plot Matrix Made Easy | Visual DNA Sequence Alignment | Solved Example
Considérations sur les Scores d'Alignement
Bien que les dot plots offrent une visualisation directe, la notion sous-jacente d'alignement de séquences repose sur des principes de "scoring". Les alignements sont "notés" selon des critères tels que :
- Score de Correspondance (Match Score) : Un score positif attribué pour chaque base ou acide aminé identique entre deux séquences.
- Pénalité de Non-correspondance (Mismatch Penalty) : Un score négatif soustrait du total pour chaque différence entre les bases ou acides aminés.
- Pénalité de Trou (Gap Penalty) : Un score négatif attribué lorsqu'une base ou un acide aminé est manquant dans l'une des séquences par rapport à l'autre (représentant des insertions ou des délétions).
Ces scores sont ajustés en fonction de l'objectif de la comparaison. Par exemple, pour rechercher de très fortes similitudes, un seuil de correspondance élevé peut être appliqué.
Conclusion Préliminaire
Le dot plot, malgré son ancienneté, demeure un outil fondamental pour la visualisation et l'analyse des relations entre séquences biologiques. Sa capacité à représenter de manière intuitive des duplications, des délétions, des insertions et des inversions en fait un complément précieux aux méthodes d'alignement quantitatives. L'évolution des outils logiciels, de la ligne de commande aux plateformes web interactives comme D-GENIES, a considérablement amélioré l'accessibilité et la puissance d'analyse des dot plots, permettant d'explorer des génomes de plus en plus vastes avec une efficacité accrue. La comparaison de plusieurs graphiques de ressemblance peut être particulièrement utile pour dégager des tendances complexes.
tags: #dot #plot #replicat #biologique
